QM/MM結構優化
QM/MM幾何構型優化計算的python腳本如下:
import glob, math, os.path
from pBabel import AmberCrdFile_ToCoordinates3,
AmberTopologyFile_ToSystem ,
SystemGeometryTrajectory ,
AmberCrdFile_FromSystem ,
PDBFile_FromSystem ,
XYZFile_FromSystem
from pCore import Clone, logFile, Selection
from pMolecule import NBModelORCA, QCModelBDF, System
from pMoleculeScripts import ConjugateGradientMinimize_SystemGeometry,
FIREMinimize_SystemGeometry ,
LBFGSMinimize_SystemGeometry ,
SteepestDescentMinimize_SystemGeometry
# 定義結構優化接口
def opt_ConjugateGradientMinimize(molecule, selection):
molecule.DefineFixedAtoms(selection) #固定原子
#定義優化方法
ConjugateGradientMinimize_SystemGeometry(
molecule,
maximumIterations = 40, # 最大優化步數
rmsGradientTolerance = 0.1, #優化收斂控制
trajectories = [(trajectory, 1)]
) # 定義軌跡保存頻率
# 定義能量計算模式
nbModel = NBModelORCA()
qcModel = QCModelBDF("GB3LYP:6-31g")
# 讀取體系坐標和拓撲信息
molecule = AmberTopologyFile_ToSystem ("GallicAcid.prmtop")
molecule.coordinates3 = AmberCrdFile_ToCoordinates3("GallicAcid.crd")
# 關閉體系對稱性
molecule.DefineSymmetry(crystalClass = None) #QM/MM方法不支持使用周期性邊界條件
#. Define Atoms List
natoms = len(molecule.atoms) # 系統中總原子數
qm_list = range(72, 90) # QM 區原子
activate_list = range(126, 144) + range (144, 162) # MM區活性原子(優化中可以移動)
#定義MM區原子
mm_list = range (natoms)
for i in qm_list:
mm_list.remove(i) # MM 刪除QM原子
mm_inactivate_list = mm_list[:]
for i in activate_list :
mm_inactivate_list.remove(i)
# 輸入QM原子
qmmmtest_qc = Selection.FromIterable(qm_list)
# 定義各選擇區
selection_qm_mm_inactivate = Selection.FromIterable(qm_list + mm_inactivate_list)
selection_mm = Selection.FromIterable(mm_list)
selection_mm_inactivate = Selection.FromIterable(mm_inactivate_list)
# . Define the energy model.
molecule.DefineQCModel(qcModel, qcSelection = qmmmtest_qc)
molecule.DefineNBModel(nbModel)
molecule.Summary()
#計算優化開始時總能量
eStart = molecule.Energy()
#定義輸出文件目錄名
outlabel = 'opt_watbox_bdf'
if os.path.exists(outlabel):
pass
else:
os.mkdir (outlabel)
outlabel = outlabel + '/' + outlabel
# 定義輸出軌跡
trajectory = SystemGeometryTrajectory (outlabel + ".trj" , molecule, mode = "w")
# 開始第一階段優化
# 定義優化兩步
iterations = 2
# 順次固定QM區和MM區進行優化
for i in range(iterations):
opt_ConjugateGradientMinimize(molecule, selection_qm_mm_inactivate) #固定QM區優化
opt_ConjugateGradientMinimize(molecule, selection_mm) #固定MM區優化
# 開始第二階段優化
# QM區和MM區同時優化
opt_ConjugateGradientMinimize(molecule, selection_mm_inactivate)
#輸出優化后總能量
eStop = molecule.Energy()
#保存優化坐標,可以為xyz/crd/pdb等。
XYZFile_FromSystem(outlabel + ".xyz", molecule)
AmberCrdFile_FromSystem(outlabel + ".crd" , molecule)
PDBFile_FromSystem(outlabel + ".pdb" , molecule)
輸出體系收斂信息如下(此處僅展示前20步優化收斂結果):
----------------------------------------------------------------------------------------------------------------
Iteration Function RMS Gradient Max. |Grad.| RMS Disp. Max. |Disp.|
----------------------------------------------------------------------------------------------------------------
0 I -1696839.69778731 2.46510318 9.94250232 0.00785674 0.03168860
2 L1s -1696839.82030342 1.38615730 5.83254788 0.00043873 0.00126431
4 L1s -1696839.90971371 1.41241184 5.29242524 0.00067556 0.00172485
6 L0s -1696840.01109863 1.41344485 4.70119338 0.00090773 0.00265969
8 L1s -1696840.09635696 1.44964059 5.72496661 0.00108731 0.00328490
10 L1s -1696840.17289698 1.28607709 4.73666387 0.00108469 0.00354577
12 L1s -1696840.23841524 1.03217304 3.00441004 0.00081945 0.00267931
14 L1s -1696840.30741088 1.40349698 5.22220965 0.00162080 0.00519590
16 L1s -1696840.43546466 1.32604042 4.51175225 0.00158796 0.00455431
18 L0s -1696840.52547251 1.27123125 4.20616166 0.00158796 0.00428040
20 L0s -1696840.60265453 1.08553355 3.12355616 0.00158796 0.00470223
----------------------------------------------------------------------------------------------------------------
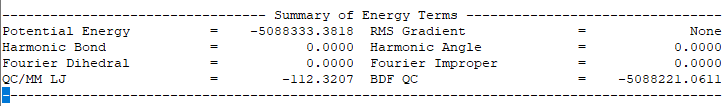
輸出體系總能量信息如下:

注:QM/MM幾何構型優化一般不容易收斂,在實際操作中需要的技巧較多。常見的有,固定MM區,優化QM區;然后固定QM區優化MM區。如此往復循環幾次后,再同時優化QM區和MM區。優化是否收斂,和QM區的選擇及QM/MM邊界是否有帶電較多的原子等關系很大。為了加速優化,可以在計算時固定MM區,僅選擇離QM區較近的合適區域,作為活性區域,在優化中坐標可以變化。
QM/MM激發態計算
基于上一步的QM/MM幾何構型優化,繼而即可將MM區活性原子添加到QM區進行QM/MM-TDDFT計算,完整的代碼如下:import glob, math, os.path
from pBabel import AmberCrdFile_ToCoordinates3,
AmberTopologyFile_ToSystem ,
SystemGeometryTrajectory ,
AmberCrdFile_FromSystem ,
PDBFile_FromSystem ,
XYZFile_FromSystem
from pCore import Clone, logFile, Selection
from pMolecule import NBModelORCA, QCModelBDF, System
from pMoleculeScripts import ConjugateGradientMinimize_SystemGeometry,
FIREMinimize_SystemGeometry ,
LBFGSMinimize_SystemGeometry ,
SteepestDescentMinimize_SystemGeometry
# 定義結構優化接口
def opt_ConjugateGradientMinimize(molecule, selection):
molecule.DefineFixedAtoms(selection) #固定原子
#定義優化方法
ConjugateGradientMinimize_SystemGeometry(
molecule,
maximumIterations = 40, # 最大優化步數
rmsGradientTolerance = 0.1, #優化收斂控制
trajectories = [(trajectory, 1)]
) # 定義軌跡保存頻率
# 定義能量計算模式
nbModel = NBModelORCA()
qcModel = QCModelBDF("GB3LYP:6-31g")
# 讀取體系坐標和拓撲信息
molecule = AmberTopologyFile_ToSystem ("GallicAcid.prmtop")
molecule.coordinates3 = AmberCrdFile_ToCoordinates3("GallicAcid.crd")
# 關閉體系對稱性
molecule.DefineSymmetry(crystalClass = None) #QM/MM方法不支持使用周期性邊界條件
#. Define Atoms List
natoms = len(molecule.atoms) # 系統中總原子數
qm_list = range(72, 90) # QM 區原子
activate_list = range(126, 144) + range (144, 162) # MM區活性原子(優化中可以移動)
#定義MM區原子
mm_list = range (natoms)
for i in qm_list:
mm_list.remove(i) # MM 刪除QM原子
mm_inactivate_list = mm_list[:]
for i in activate_list :
mm_inactivate_list.remove(i)
# 輸入QM原子
qmmmtest_qc = Selection.FromIterable(qm_list)
# 定義各選擇區
selection_qm_mm_inactivate = Selection.FromIterable(qm_list + mm_inactivate_list)
selection_mm = Selection.FromIterable(mm_list)
selection_mm_inactivate = Selection.FromIterable(mm_inactivate_list)
# . Define the energy model.
molecule.DefineQCModel(qcModel, qcSelection = qmmmtest_qc)
molecule.DefineNBModel(nbModel)
molecule.Summary()
#計算優化開始時總能量
eStart = molecule.Energy()
#定義輸出文件目錄名
outlabel = 'opt_watbox_bdf'
if os.path.exists(outlabel):
pass
else:
os.mkdir (outlabel)
outlabel = outlabel + '/' + outlabel
# 定義輸出軌跡
trajectory = SystemGeometryTrajectory (outlabel + ".trj" , molecule, mode = "w")
# 開始第一階段優化
# 定義優化兩步
iterations = 2
# 順次固定QM區和MM區進行優化
for i in range(iterations):
opt_ConjugateGradientMinimize(molecule, selection_qm_mm_inactivate) #固定QM區優化
opt_ConjugateGradientMinimize(molecule, selection_mm) #固定MM區優化
# 開始第二階段優化
# QM區和MM區同時優化
opt_ConjugateGradientMinimize(molecule, selection_mm_inactivate)
#輸出優化后總能量
eStop = molecule.Energy()
#保存優化坐標,可以為xyz/crd/pdb等。
XYZFile_FromSystem(outlabel + ".xyz", molecule)
AmberCrdFile_FromSystem(outlabel + ".crd" , molecule)
PDBFile_FromSystem(outlabel + ".pdb" , molecule)
# TDDFT計算
qcModel = QCModelBDF_template ( )
qcModel.UseTemplate (template = 'head_bdf_nosymm.inp' )
tdtest = Selection.FromIterable ( qm_list + activate_list )
# . Define the energy model.
molecule.DefineQCModel ( qcModel, qcSelection = tdtest )
molecule.DefineNBModel ( nbModel )
molecule.Summary ( )
# . Calculate
energy = molecule.Energy ( )
輸出體系總能量信息如下:
No. 1 w= 4.7116 eV -1937.8276358207 a.u. f= 0.0217 D= 0.0000 Ova= 0.6704
CV(0): A( 129 )-> A( 135 ) c_i: 0.7254 Per: 52.6% IPA: 7.721 eV Oai: 0.6606
CV(0): A( 129 )-> A( 138 ) c_i: 0.2292 Per: 5.3% IPA: 9.104 eV Oai: 0.8139
CV(0): A( 132 )-> A( 135 ) c_i: 0.4722 Per: 22.3% IPA: 7.562 eV Oai: 0.6924
CV(0): A( 132 )-> A( 138 ) c_i: -0.4062 Per: 16.5% IPA: 8.946 eV Oai: 0.6542
隨后還打印了躍遷偶極矩
*** Ground to excited state Transition electric dipole moments (Au) ***
State X Y Z Osc.
1 0.0959 0.1531 0.3937 0.0217 0.0217
2 0.0632 -0.1286 0.3984 0.0207 0.0207
3 -0.0797 -0.2409 0.4272 0.0287 0.0287
4 0.0384 -0.0172 -0.0189 0.0003 0.0003
5 1.1981 0.8618 -0.1305 0.2751 0.2751
吸收光譜分析
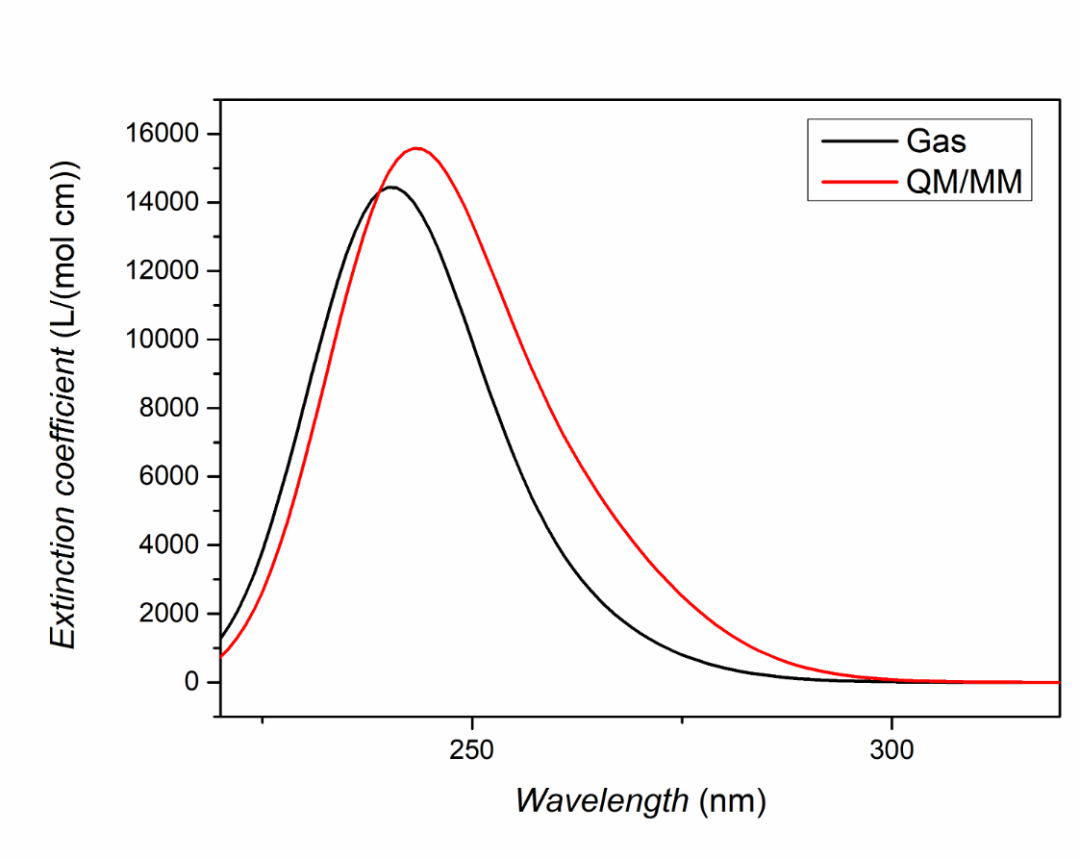
對于激發態我們往往需要得到理論預測的吸收譜峰形,也就是將每個激發態的吸收按一定的半峰寬進行高斯展寬。在TDDFT計算正常結束后,我們需要進入終端用命令調用BDF安裝路徑下的plotspec.py腳本執行計算。若用戶使用鴻之微云算力資源,進入命令端方式請查閱鴻之微云指南,此文不做贅述。
進入終端后,在目錄下運行$BDFHOME/sbin/plotspec.py bdf.out,會產生兩個文件,分別為bdf.stick.csv和bdf.spec.csv,前者包含所有激發態的吸收波長和摩爾消光系數,可以用來作棒狀圖,后者包含高斯展寬后的吸收譜(默認的展寬FWHM為0.5 eV),分別對比真空環境以及溶劑化效應下高斯展寬后的吸收譜情況,并用Excel、Origin等作圖軟件作圖如下:
-
光譜分析
+關注
關注
0文章
41瀏覽量
10380 -
python
+關注
關注
57文章
4876瀏覽量
90025
原文標題:鴻之微BDF軟件計算賞析|采用BDF的QM/MM多尺度計算方法研究晶體的光物理性質(二)
文章出處:【微信號:hzwtech,微信公眾號:鴻之微】歡迎添加關注!文章轉載請注明出處。
發布評論請先 登錄
官方新品 | 虹科PCAN-Explorer 7發布:帶來Python腳本與靈活授權新體驗

光子精密QM系列閃測儀優化VR眼鏡關鍵制程質量控制

用 Python 給 Amazon 做“全身 CT”——可量產、可擴展的商品詳情爬蟲實戰
Pico Technology發布Python軟件包pyPicoSDK
高效高精度!光子精密QM系列閃測儀電子外殼尺寸檢測案例

termux調試python猜數字游戲
termux如何搭建python游戲
Python腳本實現運維工作自動化案例
FRED應用:MTF的計算
請問如何在imx8qm上將PCIe和SMMU用于顯卡?
零基礎入門:如何在樹莓派上編寫和運行Python程序?




 QM/MM幾何構型優化計算的python腳本
QM/MM幾何構型優化計算的python腳本





評論